Antes de continuar a leitura do texto, quero te convidar para conhecer meus cursos:
- Hematologia básica clique aqui
- Anemias clique aqui
- Onco-hematologia clique aqui
- Interpretando o hemograma clique aqui
- Curso de Hematologia (10% off) clique aqui
- Preparatório de Análises Clínicas para Residência e Concurso clique aqui
Continue agora com a sua leitura do texto. Espero que goste.
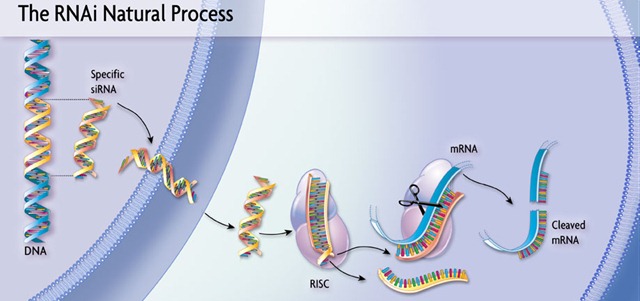
A interferência por RNA (RNAi) é um mecanismo celular responsável pelo silenciamento gênico pós-transcricional que atua sobre o RNA mensageiro (mRNA), ou seja, é esse mecanismo que determinará o fim da vida útil do mRNA, para que não sejam produzidas proteínas além do necessário.
Envolvida neste mecanismo está uma molécula de fita dupla de RNA (dsRNA - double stranded RNA) que, ao ser incorporada na forma ativa a um complexo no citoplasma, se liga a uma sequência de nucleotídeos complementar localizada no mRNA-alvo, ocasionando assim o silenciamento, por inibição da tradução e/ou degradação do mRNA.
Em 2006, os pesquisadores norte-americanos, Andrew Z. Fire e Craig C. Mello foram contemplados com o prêmio Nobel de Medicina e Fisiologia por sua participação na elucidação do silenciamento gênico por RNAi.
O processo de interferência de RNA, que leva à clivagem de um mRNA específico ou ao bloqueio da síntese de proteínas a partir deste mRNA, pode começar:
- pela injeção de um RNA fita dupla (dsRNA);
- pela síntese de um RNA que forme um longo grampo (a partir da transcrição de um trecho de DNA genômico ou de um transgene, engenheirado para isso e inserido no genoma do organismo), ou;
- pela síntese de um RNA de interferência, que será clivado pela enzima Drosha no núcleo, gerando um grampo que será, no citoplasma, clivado de novo pela enzima Dicer.
Quando gera-se um RNA fita dupla no citoplasma (por qualquer um dos 3 caminhos citados acima), as enzimas Dicer vão cortá-lo em pelo menos um fragmento de 21 pb.
Os pequenos fragmentos de dsRNA são então carregados num complexo enzimático formado pela enzima Argonauta e algumas outras enzimas, como uma helicase e uma enzima com domínio ligador de dsRNA, chamada R2D2.
Um das subunidades leva embora uma das fitas de RNA e a outra (em geral, a complementar ao mRNA alvo da futura clivagem), fica. Há um mecanismo de instabilidade da região 5´ do dsRNA que favorece a permanência da fita complementar no complexo.
O passo seguinte do caminho para a interferência é o pareamento entre o RNA fita simples contido na Argonauta e o mRNA alvo. A probabilidade de um pareamento errôneo é muito remota, já que é preciso que haja o pareamento exato de pelo menos 19 das bases. Assim que o pareamento for feito, duas coisas podem ocorrer:
- se o mRNA não estiver sendo traduzido, ele será clivado.
- se o mRNA estiver sendo traduzido, o Argonauta se liga a ele e leva a um bloqueio da tradução.
Em ambos os casos não vai haver mais a síntese de proteínas a partir do mRNA-alvo. Este é o objetivo da interferência de RNA.
Fontes:
Interferência de RNA
Interferência por RNA: Uma nova alternativa para terapia nas doenças reumáticas





